Uma proteína em forma de donut se quebra para iniciar a divisão celular bacteriana
Uma equipe de pesquisa liderada pelo cientista da Universidade Autônoma de Barcelona (UAB), David Reverter, identificou o mecanismo molecular que regula a divisão celular bacteriana. A descoberta revela como a proteína MraZ se liga ao cluster do gene dcw para controlar este processo. As descobertas foram publicadas em Comunicações da Natureza.
A divisão celular é essencial para todos os organismos vivos e depende da atividade coordenada de muitas proteínas e componentes reguladores. Na maioria das bactérias, as instruções para esse processo são organizadas dentro de um grupo de genes conhecido como operon dcw. Este cluster contém a informação genética necessária para produzir proteínas responsáveis tanto pela divisão celular como pela construção da parede celular bacteriana.
Como o operon dcw ativa os genes da divisão celular
Os genes neste cluster são ativados por proteínas conhecidas como fatores de transcrição. Essas proteínas se ligam a uma seção específica do DNA chamada promotor, que marca onde a transcrição começa. Este ponto de partida aparece logo antes do primeiro códon (a unidade básica da informação genética) que sinaliza o início da sequência da proteína.
Um desses fatores de transcrição é o MraZ, que também é o primeiro gene dentro do operon dcw em todas as bactérias. Quando MraZ ativa o operon, os genes dentro do cluster produzem as proteínas necessárias para a divisão das bactérias. Desta forma, o MraZ atua como o principal regulador que controla a atividade do operon que governa a divisão celular na maioria das espécies bacterianas.
Imagem do mecanismo molecular da divisão bacteriana
O grupo de investigação da UAB, liderado por David Reverter, professor catedrático do Departamento de Bioquímica e Biologia Molecular e investigador do Instituto de Biotecnologia e Biomedicina da UAB (IBB-UAB), descobriu o mecanismo detalhado por detrás desta regulação. A equipe usou métodos avançados de biologia estrutural, incluindo cristalografia de raios X e microscopia crioeletrônica.
Essas técnicas permitiram aos cientistas determinar como o fator de transcrição MraZ se liga ao promotor do operon dcw na bactéria Micoplasma genitalium. Esse microrganismo é frequentemente utilizado em estudos de laboratório por possuir um genoma extremamente pequeno.
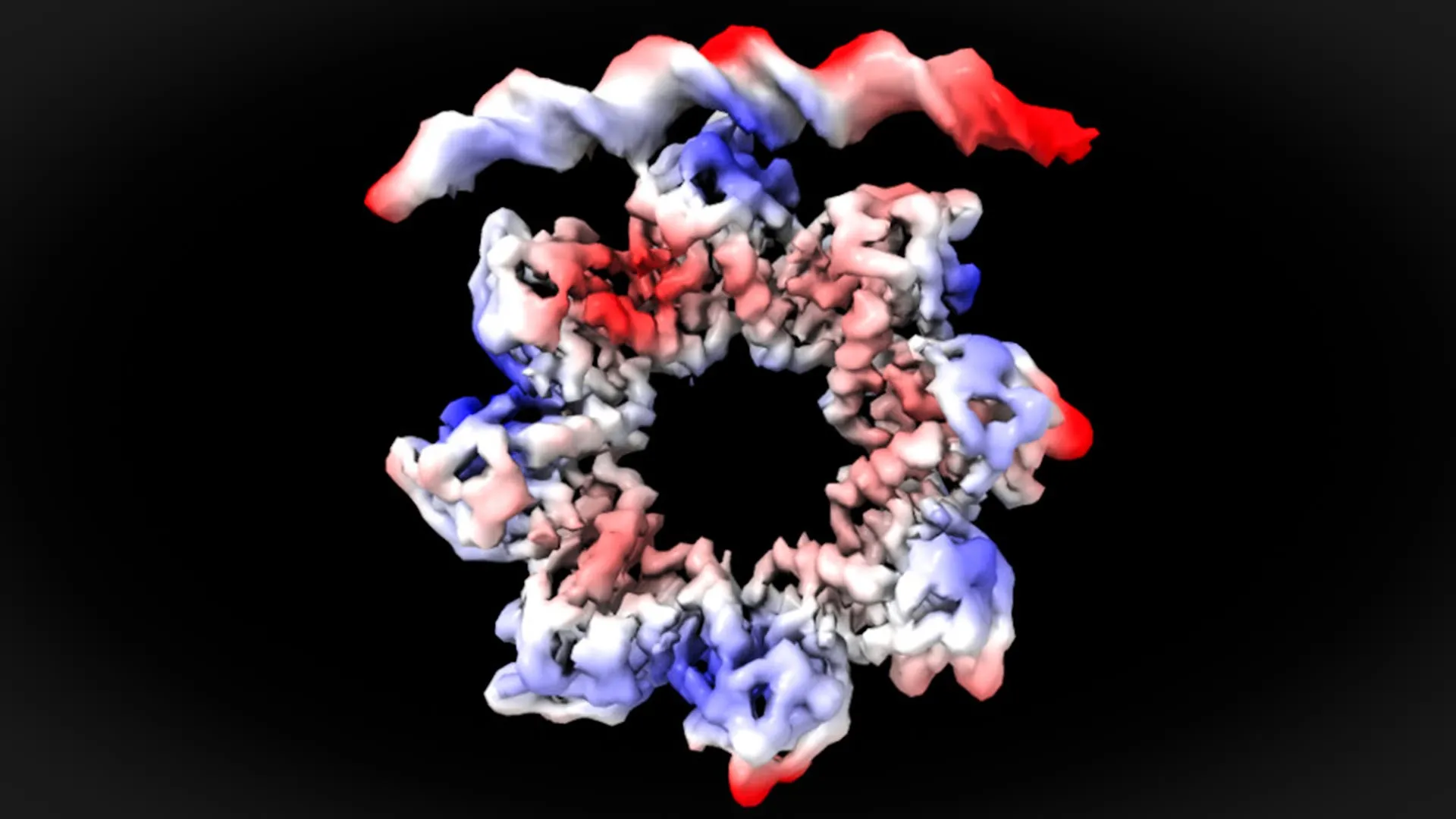
Visão em nível atômico do DNA de ligação à proteína MraZ
A região promotora do operon dcw contém quatro segmentos repetidos, ou “caixas”, cada um composto por seis nucleotídeos. Estas sequências repetidas de DNA desempenham um papel fundamental na regulação da transcrição.
Ao examinar o sistema com microscopia crioeletrônica, os pesquisadores conseguiram observar a interação entre a proteína MraZ e as bases de DNA dessas quatro caixas repetidas em resolução quase atômica. Suas observações mostraram que o MraZ deve passar por uma mudança estrutural para se ligar com sucesso ao operon.
“Esta é uma observação surpreendente. A proteína MraZ é um octâmero formado por oito subunidades idênticas unidas em forma de donut, mas com uma curvatura que nunca permitiria a união com as quatro ‘caixas’ do promotor. Porém, para regular a divisão celular vemos como o donut se quebra e se deforma de tal forma que quatro das subunidades podem se juntar às quatro caixas do promotor”, explica David Reverter.
Um grande avanço na compreensão da divisão celular bacteriana
A visualização direta de como o MraZ interage com o DNA promotor que inicia a divisão celular representa um avanço significativo. Até agora, os investigadores que estudam este sistema basearam-se em grande parte em experiências bioquímicas e modelos computacionais para inferir como o mecanismo funcionava.
Segundo Reverter, o sistema regulatório identificado neste estudo é provavelmente difundido entre as bactérias. “é universal para a maioria das bactérias, pois todas as proteínas MraZ são muito semelhantes, têm a mesma estrutura de octâmero e as sequências de DNA dos promotores dos operons que regulam a divisão celular também são semelhantes”, conclui Reverter.
Colaboração internacional por trás do estudo
A pesquisa foi liderada pela equipe de David Reverter do Instituto de Biotecnologia e Biomedicina e do Departamento de Bioquímica e Biologia Molecular da UAB. O trabalho foi realizado em colaboração com o síncrotron ALBA e o serviço de microscopia crioeletrônica do Instituto de Genética e Biologia Molecular e Celular de Estrasburgo, França.
Share this content:



Publicar comentário